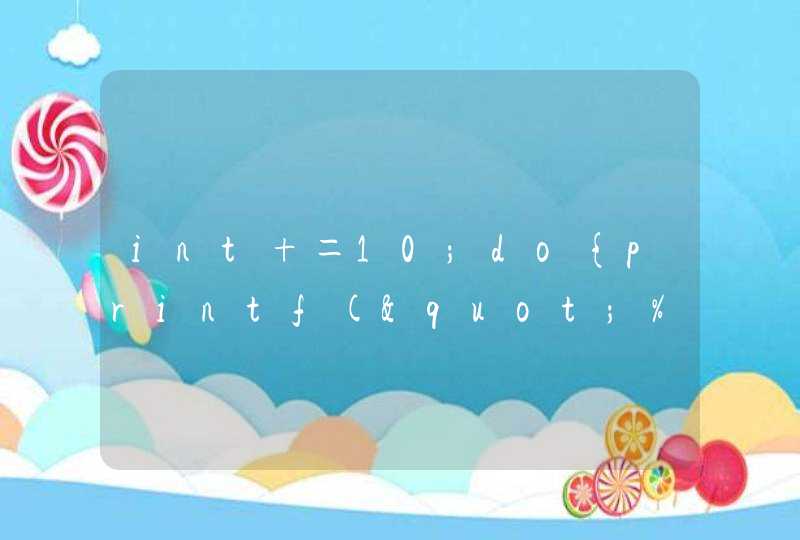cl.cores <- detectCores()
cl<- makeCluster(cl.cores)
detectCores()检查当前电脑可用核数。
makeCluster(cl.cores)使用刚才检测的核并行运算。R-Doc里这样描述makeCluster函数:Creates a set of copies of R running in parallel andcommunicating over sockets. 即同时创建数个R进行并行运算。在该函数执行后就已经开始并行运算了,电脑可能会变卡一点。尤其在执行par开头的函数时。
在并行运算环境下,常用的一些计算方法如下:
1. clusterEvalQ(cl,expr)函数利用创建的cl执行expr。这里利用刚才创建的cl核并行运算expr。expr是执行命令的语句,不过如果命令太长的话,一般写到文件里比较好。比如把想执行的命令放在Rcode.r里:
clusterEvalQ(cl,source(file="Rcode.r"))
2.par开头的apply函数族。这族函数和apply的用法基本一样,不过要多加一个参数cl。一般如果cl创建如上面cl <-makeCluster(cl.cores)的话,这个参数可以直接用作parApply(cl=cl,…)。当然Apply也可以是Sapply,Lapply等等。注意par后面的第一个字母是要大写的,而一般的apply函数族第一个字母不大写。
另外要注意,即使构建了并行运算的核,不使用parApply()函数,而使用apply()函数的话,则仍然没有实现并行运算。换句话说,makeCluster只是创建了待用的核,而不是并行运算的环境。
最后,终止并行运算只需要一行命令:
stopCluster(cl)
当参数no.readonly=TRUE时,函数par()就只允许有这一个参数了,并且会返回当前绘图设备中各个参数的参数值。 每一个图形设备都有自己的绘图参数,如果当前还没有打开绘图设备,那么函数par()在进行参数设置之前会自动的打开一个新绘图设备。如前面所说,直接在R编辑器中输入命令par()或者par(no.readonly=TRUE)都可以获取当前的各个绘图参数。
1、符号和线条
2、颜色
3、文本属性(用来指定字号、字体、字样)
4、图形尺寸与图形边界
5、标题
也可以直接把title里面的参数直接放在plot()里面
6、坐标轴
plot参数
例如:plot(1:10, xlim = c(-10, 10), ylim = c(0, 10)) xlim和ylim只是坐标轴的范围,与每个点的x和y坐标没有关系,也可以通过axis函数自定义axis(……)
side:一个整数。表示在图形的哪边绘制坐标轴(1=下,2=左,3=上,4=右)
7、参考线
例如:plot(1:10)
8、图例(legend)
待续……